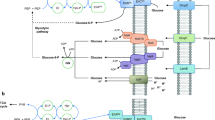
Abstract
The gram-negative bacterium Pseudomonas putida is of increasing interest for industrial applications due to its intrinsic resistance to a broad range of stresses, its metabolic versatility, and the availability of genetic tools. Our group aims to introduce new metabolic pathways by genetic engineering to further expand the metabolic spectrum of this microorganism. Here, we summarize the process of engineering a sucrose consuming strain of P. putida, the obstacles found on the way, and how they were overcome to achieve a stable phenotype.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Nikel PI, Chavarría M, Danchin A, de Lorenzo V (2016) From dirt to industrial applications: Pseudomonas putida as a synthetic biology chassis for hosting harsh biochemical reactions. Curr Opin Chem Biol 34: 20–29
Poblete-Castro I, de Acuña JMB, Nikel PI et al. (2017) Host organism: Pseudomonas putida. In: Wittmann C, Liao JC (Hrsg.) Industrial biotechnology: Microorganisms. Volume 1, Wiley-VCH Verlag, New York, 299–326
Nikel PI, de Lorenzo V (2018) Pseudomonas putida as a functional chassis for industrial biocatalysis: from native biochemistry to trans-metabolism. Metab Eng 50: 142–155
Nikel PI, Martínez-García E, de Lorenzo V (2014) Biotechnological domestication of pseudomonads using synthetic biology. Nat Rev Microbiol 12: 368–379
Nikel PI, Chavarría M, Führer T et al. (2015) Pseudomonas putida KT2440 strain metabolizes glucose through a cycle formed by enzymes of the Entner-Doudoroff, Embden-Meyerhof-Parnas, and pentose phosphate pathways. J Biol Chem 290: 25920–25932
Nikel PI, Fuhrer T, Chavarría M et al. (2021) Reconfiguration of metabolic fluxes in Pseudomonas putida as a response to sub-lethal oxidative stress. Isme J, doi: https://doi.org/10.1038/s41396-020-00884-9
Sabri S, Nielsen LK, Vickers CE (2012) Molecular control of sucrose utilization in Escherichia coli W, an efficient sucrose-utilizing strain. Appl Environ Microbiol 79: 478–487
Löwe H, Schmauder L, Hobmeier K et al. (2017) Metabolic engineering to expand the substrate spectrum of Pseudomonas putida toward sucrose. MicrobiologyOpen 6: e00473
Hancock REW, Brinkman FSL (2002) Function of Pseudomonas porins in uptake and efflux. Annu Rev Microbiol 56: 17–38
Thompson DK, Chourey K, Wickham GS et al. (2010) Proteomics reveals a core molecular response of Pseudomonas putida F1 to acute chromate challenge. BMC Genomics 11: 311
Choi C-W, Park EC, Yun SH et al. (2014) Proteomic characterization of the outer membrane vesicle of Pseudomonas putida KT2440. J Proteome Res 13: 4298–4309
Löwe H, Sinner P, Kremling A, Pflüger-Grau K (2018) Engineering sucrose metabolism in Pseudomonas putida highlights the importance of porins. Microb Biotechnol 13: 97–106
Sawyer MH, Baumann P, Baumann L et al. (1977) Pathways of D-fructose catabolism in species of Pseudomonas. Arch Microbiol 112: 49–55
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Unser Dank gilt Prof. Kirsten Jung (LMU, München) für die Überlassung von Pseudomonas protegens Pf-5 und Víctor de Lorenzo (CNB, Madrid) für die Plasmide aus der SEVA Bibliothek. Ein besonderer Dank geht an Karina Hobmeier, Lukas Schmauder und Peter Sinner, die an der Bearbeitung dieses Themas beteiligt waren.
Funding note
Open Access funding enabled and organized by Projekt DEAL.
Hannes Löwe, Andreas Kremling und Katharina Pflüger-Grau (v. l. n. r.)
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Löwe, H., Kremling, A. & Pflüger-Grau, K. Friss oder stirb! Erweiterung des Substratspektrums von P. putida. Biospektrum 27, 322–325 (2021). https://doi.org/10.1007/s12268-021-1568-6
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-021-1568-6