Abstract
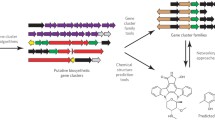
Bacteria produce natural products to interact with their environment. These structurally diverse small molecules exhibit various bioactivities and have been exploited for the treatment of many diseases. The discovery pace of truly novel natural products using traditional methods has markedly declined. As an alternative, sophisticated bioinformatic tools have been developed that leverage genome sequence information for the targeted discovery of bioactive compounds. To chart microbial biosynthetic dark matter and identify non-canonical natural product biosynthetic pathways that escape unrecognised by current bioinformatic tools, artificial intelligence has recently been introduced into the genome mining process, holding promise to expand natural product chemical and biosynthetic space.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Medema MH, Rond T de, Moore BS (2021) Mining genomes to illuminate the specialized chemistry of life. Nat Rev Genet 22: 553–571
Scott TA, Piel J (2019) The hidden enzymology of bacterial natural product biosynthesis. Nat Rev Chem 3: 404–425
Weber T (2014) In silico tools for the analysis of antibiotic biosynthetic pathways. Int J Med Microbiol 304: 230–235
Ziemert N, Alanjary M, Weber T (2016) The evolution of genome mining in microbes - a review. Nat Prod Rep 33: 988–1005
Biermann F, Helfrich EJN (2021) Hidden treasures: Microbial natural product biosynthesis off the beaten path. mSystems: e0084621
Nanudorn P, Thiengmag S, Biermann F et al. (2022) Atropopeptides are a novel family of ribosomally synthesized and posttranslationally modified peptides with a complex molecular shape. Angew Chem Int Ed 61: e202208361
Reisberg SH, Gao Y, Walker A et al. (2020) Total synthesis reveals atypical atropisomerism in a small-molecule natural product, tryptorubin A. Science 367: 458–463
Biermann F, Tan B, Breitenbach M et al. (2023) Machine learning-based exploration, expansion and definition of the atropopeptide family of ribosomally synthesized and post-translationally modified peptides. bioRxiv: 2023.11.03.565440
Funding
Funding note: Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Ein besonderer Dank geht an unsere Arbeitsgruppe für den konstruktiven Austausch von Fachwissen aus verschiedenen Disziplinen. Darüber hinaus möchten wir dem LOEWE-Zentrum für Translationale Biodiversitätsgenomik und dem Emmy-Noether-Programm der Deutschen Forschungsgemeinschaft für die Bereitstellung der finanziellen Mittel für unsere Forschungdanken.
Thao Phan
2013–2019 Studium der Biowissenschaften und Molekularen Biotechnologie an der Universität Frankfurt a. M. 2018–2019 Forschungsaufenthalt an der Katholieke Universiteit Leuven, Belgien. 2020–2021 wissenschaftliche Mitarbeiterin am Leibniz-Institut für Neue Materialien, Saarbrücken und an der Universität Frankfurt a. M. Seit 2022 Doktorandin am Institut für Molekulare Biowissenschaften der Universität Frankfurt a. M.
Julia Spies
2017–2021 Bachelorstudium der Biowissenschaften und 2020–2022 Masterstudium der Molekulare Biowissenschaften an der Universität Frankfurt a. M. Seit 2023 Promotions-studentin am Institut für Molekulare Biowissenschaften der Universität Frankfurt a. M.
Milena Breitenbach
2016–2020 Studium der Biowissenschaften an der Hochschule Fresenius. 2020–2021 Studium der Bioanalytik an der Hochschule Fresenius. 2021–2022 beschäftigt bei A&M Stabtest Mainz. Seit 2022 wissenschaftliche Mitarbeiterin an der Universität Frankfurt a. M.
Eric Helfrich
2007–2010 Bachelorstudium in Molekularer Biomedizin, Universität Bonn. 2010–2013 Masterstudium in Chemischer Biologie, Universität Jena. 2013–2017 Promotion an der Eidgenössischen Technischen Hochschule (ETH) in Zürich, Schweiz. 2018–2020 PostDoc an der Harvard Medical School, Boston, USA. Seit 2020 W1-tt-W2 Professor für Naturstoffgenomik an der Universität Frankfurt und dem LOEWE Zentrum für translationale Biodiversitätsgenomik in Frankfurt a. M.
Rights and permissions
Open Access: Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Phan, T.N., Spies, J., Breitebach, M. et al. Genombasierte Wege zur Identifikation bioaktiver bakterieller Naturstoffe. Biospektrum 30, 264–267 (2024). https://doi.org/10.1007/s12268-024-2192-z
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-024-2192-z