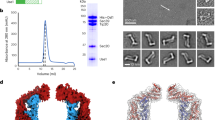
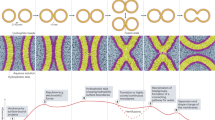
Abstract
Almost all eukaryotic membrane proteins start their life in the cytosol and must journey to the cellular membrane where they function, most often via the ER. The cell employs multiple pathways to target and insert different classes of membrane proteins into the ER membrane, including the recently discovered SND pathway. Whilst the key players of the SND pathway are characterised, fundamental questions remain as to how these proteins cooperate to deliver a broad range of substrates to the ER.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Chartron JW, Hunt KCL, Frydman J (2016) Cotranslational signal-independent SRP preloading during membrane targeting. Nature 536: 224–228
Ast T, Schuldiner M (2013) All roads lead to Rome (but some may be harder to travel): SRP-independent translocation into the endoplasmic reticulum. Critical Reviews in Biochemistry and Molecular Biology 48: 273–288
Hann BC, Walter P (1991) The signal recognition particle in S. cerevisiae. Cell 67: 131–144
Schuldiner M, Metz J, Schmid V et al. (2008) The GET complex mediates insertion of tail-anchored proteins into the ER membrane. Cell 134: 634–645
Aviram N, Ast T, Costa EA et al. (2016) The SND proteins constitute an alternative targeting route to the endoplasmic reticulum. Nature 540: 134–138
Yang J, Hirata T, Liu Y-S et al. (2021) Human SND2 mediates ER targeting of GPI-anchored proteins with low hydrophobic GPI attachment signals. FEBS Letters 595: 1542–1558
Haßdenteufel S, Johnson N, Paton AW et al. (2018) Chaperone-mediated Sec61 channel gating during ER import of small precursor proteins overcomes Sec61 inhibitor-reinforced energy barrier. Cell Reports 23: 1373–1386
Haßdenteufel S, Sicking M, Schorr S et al. (2017) hSnd2 protein represents an alternative targeting factor to the endoplasmic reticulum in human cells. FEBS Letters 591: 3211–3224
Tirincsi A, O'Keefe S, Nguyen D et al. (2022) Proteomics identifies substrates and a novel component in hSnd2-dependent ER protein targeting. Cells 11: 2925
Fleischer TC, Weaver CM, McAfee KJ et al. (2006) Systematic identification and functional screens of uncharacterized proteins associated with eukaryotic ribosomal complexes. Genes & Development 20: 1294–1307
Liaci AM, Förster F (2021) Take me home, protein roads: Structural insights into signal peptide interactions during ER translocation. Int J Mol Sci 22: 11871
McDowell MA, Heimes M, Sinning I (2021) Structural and molecular mechanisms for membrane protein biogenesis by the Oxa1 superfamily. Nat Struct Mol Biol 28: 234–239
Gemmer M, Förster F (2020) A clearer picture of the ER translocon complex. J Cell Sci 133: jcs231340
Venturi E, Mio K, Nishi M et al. (2011) Mitsugumin 23 Forms a Massive Bowl-Shaped Assembly and Cation-Conducting Channel. Biochemistry 50: 2623–2632
Tosal-Castano S, Peselj C, Kohler V et al. (2021) Snd3 controls nucleus-vacuole junctions in response to glucose signaling. Cell Rep 34: 108637
Jumper J, Evans R, Pritzel A et al. (2021) Highly accurate protein structure prediction with AlphaFold. Nature 596: 583–589
Varadi M, Anyango S, Deshpande M et al. (2022) AlphaFold Protein Structure Database: massively expanding the structural coverage of protein-sequence space with high-accuracy models. Nucleic Acids Res 50: D439–D444
Funding
Funding note: Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Ich bin Dr. Jeremy Sloan (BASF, Ludwigshafen am Rhein) sehr dankbar für seine Hilfe mit der deutschen Übersetzung.
Melanie A. McDowell
2004–2008 Biochemiestudium an der Universität Oxford, UK; dort bis 2012 Promotion in Strukturbiologie und 2012–2014 Postdoc, beide im Labor von Prof. Dr. S. Lea. 2014–2021 Postdoktorandin an der Universität Heidelberg mit Prof. Dr. I. Sinning. Seit 2022 Forschungsgruppenleiterin am Max-Planck-Institut für Biophysik in Frankfurt a. M.
Rights and permissions
Open Access: Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
McDowell, M.A. Der mysteriöse SND-Weg beim Membranproteintransport. Biospektrum 29, 442–445 (2023). https://doi.org/10.1007/s12268-023-1951-6
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-023-1951-6