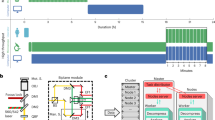
Abstract
Cellular response to perturbations, if examined at the single cell level, exhibits cell-to-cell differences, distinct dynamic behavior and correlations meaningful for the study of regulatory networks and information processing. Live-cell imaging on single cell arrays (LISCA) facilitates automated acquisition of individual time courses with sharp temporal resolution. Here we discuss expression dynamics after transient GFP transfection and event-time correlations in nanoparticle induced apotosis.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Locke JC, Elowitz MB (2009) Using movies to analyse gene circuit dynamics in single cells. Nat Rev Microbiol 7: 383–392
Snijder B, Pelkmands L (2011) Origins of regulated cell-to-cell variability. Nat Rev Mol Cell Biol 12: 119–125
Altschuler SJ, Wu LF (2010) Cellular heterogeneity: Do differences make a difference? Cell 141: 559–563
Caicedo JC, Cooper S, Heigwer F et al. (2017) Data-analysis strategies for image-based cell profiling. Nat Methods 14: 849–863
Fink J, Thery M, Azioune A et al. (2007) Comparative study and improvement of current cell micro-patterning techniques. Lab Chip 7: 672–680
Reiser A, Woschée D, Kempe S et al. (2021) Live-cell imaging of single-cell arrays (LISCA) — a versatile technique to quantify cellular kinetics. J Vis Exp 169, DOI: https://doi.org/10.3791/62025
Woschée D (2020) Github PyAMA. https://github.com/SoftmatterLMU-RaedlerGroup/pyama
Ferizi M, Leonhardt C, Meggle C (2015) Stability analysis of chemically modified mRNA using micropattern-based single-cell arrays. Lab Chip 15: 3561–3571
Krzyszton R, Woschée DW, Reiser A et al. (2019) Single-cell kinetics of siRNA-mediated mRNA degradation. Nanomedicine 21: 102077
Reiser A, Woschée D, Mehrotra N et al. (2019) Correlation of mRNA delivery timing and protein expression in lipid-based transfection. Integr Biol (Camb) 11: 362–371
Murschhauser A, Röttgermann PJF, Woschée D et al. (2019) A high-throughput microscopy method for single-cell analysis of event-time correlations in nanoparticle induced cell death. Commun Biol 2: 35
Funding
Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Dieses Projekt wurde durch die Bayerische Stiftungsförderung gefördert.
Judith Müller 2012–2017 Nanowissenschaftsstudium an der Universität Basel, Schweiz. 2017–2021 Anstellung bei der Firma ethris. Seit 2021 Promotionskandiatin an der LMU München, AG Rädler.
Gerlinde Schwake 1993–1998 Biotechnologiestudium an der FH Weihenstephan. 1999–2002 Research Scientist bei EPIDAUROS Biotechnologie AG in der Pharmakogenetik. Seit 2003 Wissenschaftlerin an der LMU München, AG Rädler.
Joachim Rädler 1984–1989 Physikstudium. 1993 Promotion in Biophysik unter Leitung von Prof. Dr. Erich Sackmann. 1993–1996 Postdoktorand bei Prof. Dr. Cyrus Safinya, University of Califoria, Santa Barbara, USA. 1996–2000 Habilitation TU München. 2000 Gruppenleiterstellung am Max-Planck-Institut für Polymerforschung, Mainz. Seit 2001 Ordinarius an der LMU München und Mitglied des Center for NanoScience. Cofounder und Advisory Board Member ibidi GmbH.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Müller, J.A., Schwake, G. & Rädler, J.O. Einzelzellmikroskopie im Hochdurchsatz auf Mikrostrukturen. Biospektrum 28, 723–725 (2022). https://doi.org/10.1007/s12268-022-1857-8
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1857-8