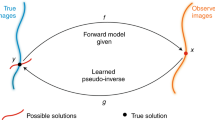
Abstract
Fluorescence live cell microscopy is central to the analysis of inter- and intracellular signaling. However, analysis of highly dynamic, local processes requires high temporal and spatial resolution imaging, which is intrinsically linked to a low signal-to-noise ratio. To improve image quality after data acquisition, computational techniques, referred to as deconvolution, are being developed. Here, we discuss recent approaches in the areas of variational and deep learning image deconvolution.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Brock VJ, Wolf IMA, Er-Lukowiak M et al. (2022) P2X4 and P2X7 are essential players in basal T cell activity and Ca2+ signaling milliseconds after T cell activation. Sci Adv 8: eabl9770
Diercks BP, Werner R, Weidemüller P et al. (2018) ORAI1, STIM1/2, and RYR1 shape subsecond Ca2+ microdomains upon T cell activation. Sci Signal 11: eaat0358
Makarkin M, Bratashov D (2021) State-of-the-art approaches for image deconvolution problems, including modern deep learning architectures. Micromachines 12: 1558
Sage D, Donati L, Soulez F et al. (2017) DeconvolutionLab2: An open-source software for deconvolution microscopy. Methods 115: 28–41
Arigovindan M, Fung JC, Elnatan D et al. (2013) High-resolution restoration of 3D structures from widefield images with extreme low signal-to-noise-ratio. Proc Natl Acad Sci USA 110: 17344–17349
Woelk LM, Kannabiran SA, Brock VJ et al. (2021) Time-dependent image restoration of low-SNR live-cell Ca2+ fluorescence microscopy data. Int J Mol Sci 22: 11792
Zhao W, Zhao S, Li L et al. (2022) Sparse deconvolution improves the resolution of live-cell super-resolution fluorescence microscopy. Nat Biotechnol 40: 606–617
Weigert M, Schmidt U, Boothe T et al. (2018) Content-aware image restoration: pushing the limits of fluorescence microscopy. Nat Methods 15: 1090–1097
Wang H, Rivenson Y, Jin Y et al. (2019) Deep learning enables cross-modality super-resolution in fluorescence microscopy. Nat Methods 16: 103–110
Chen J, Sasaki H, Lai H et al. (2021) Three-dimensional residual channel attention networks denoise and sharpen fluorescence microscopy image volumes. Nat Methods 18: 678–687
Belthangady C, Royer LA (2019) Applications, promises, and pitfalls of deep learning for fluorescence image reconstruction. Nat Methods 16: 1215–1225
Funding
Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Gefördert durch die Deutsche Forschungsgemeinschaft (SFB 1328/2, Projekt A02, Projektnr. 335447717).
Lena-Marie Woelk 2009–2015 Physikstudium an der Universität Hamburg. Dort 2016–2019 Promotion in Theoretischer Festkörperphysik. Seit 2019 Postdoktorandin im Bereich Medizinische Bildverarbeitung am Institut für Computational Neuroscience (ICNS) des Universitätsklinikums Hamburg-Eppendorf (UKE).
Björn-Philipp Diercks 2007–2012 Biologiestudium (B.Sc., M.Sc.) an der Universität Hamburg mit anschließender Promotion am Institut für Biochemie und Molekulare Zellbiologie (IBMZ) des Universitätsklinikums Hamburg-Eppendorf. Seit 2020 Arbeitsgruppenleiter am IBMZ.
René Werner 1999–2005 Informatik- und 2001–2008 Physikstudium an der Universität Hamburg. 2012 Promotion in Informatik an der Universität zu Lübeck. 2012–2015 Postdoktorand und seit 2015 Arbeitsgruppenleiter für Medizinische Bildverarbeitung am Institut für Computational Neuroscience (ICNS) des Universitätsklinikums Hamburg-Eppendorf.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Woelk, LM., Diercks, BP. & Werner, R. Dekonvolution von Mikroskopiedaten bei niedrigem Signal-Rausch-Verhältnis. Biospektrum 28, 720–722 (2022). https://doi.org/10.1007/s12268-022-1850-2
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1850-2