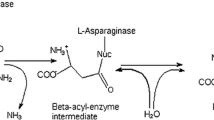
Abstract
Repurposing the enzymes in microbial metabolism such as nonribosomal peptide synthetases (NRPSs) is explored as a route towards better antibiotics. NRPSs are gigantic enzymatic assembly lines that form highly modified peptides from diverse building blocks. A novel hydroxamate assay detects full substrate profiles of NRPSs from cell-like substrate mixtures. Facile recording of substrate profiles has applications in natural product discovery and engineering.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Stanišić A, Kries H (2019) Adenylation domains in nonribosomal peptide engineering. ChemBioChem 20: 1347–1356
Stanišić A, Hüsken A, Kries H (2019) HAMA: a multiplexed LC-MS/MS assay for specificity profiling of adenylate-forming enzymes. Chem Sci 10: 10395–10399
Wurlitzer JM, Stanišić A, Wasmuth I et al. (2021) Bacterial-like nonribosomal peptide synthetases produce cyclopeptides in the zygomycetous fungus Mortierella alpina. Appl Environ Microbiol 87: e02051–20
Wurlitzer JM, Stanišić A, Ziethe S et al. (2022) Macrophage-targeting oligopeptides from Mortierella alpina. Chem Sci, DOI: https://doi.org/10.1039/d2sc00860b
Stanišić A, Hüsken A, Stephan P et al. (2021) Engineered nonribosomal peptide synthetase shows opposite amino acid loading and condensation specificity. ACS Catal 11: 8692–8700
Funding
Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Wir bedanken uns für die Unterstützung durch die Deutsche Forschungsgemeinschaft, die Max-Buchner-Forschungsstiftung, die Daimler und Benz Stiftung, den Fonds der Chemischen Industrie und die Leibniz-Gemeinschaft.
Markus Gressler Jahrgang 1984. Biochemiestudium an der Universität Jena. 2015 Promotion. 2015–2017 Postdoc am Pasteur-Institut, Paris, Frankreich. Seit 2017 wissenschaftlicher Mitarbeiter am Institut für Pharmazie an der Universität Jena.
Hajo Kries Jahrgang 1983. Biochemiestudium an den Universitäten Jena und Genf sowie Chemiestudium an der ETH Zürich, Schweiz. 2014 Promotion. 2014–2016 Postdoc am John-Innes-Centre in Norwich, UK. Seit 2016 Nachwuchsgruppenleiter am Leibniz-Institut für Naturstoff-Forschung und Infektionsbiologie, Jena.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Gressler, M., Kries, H. Mikrobielle Antibiotikafabriken verstehen und verbessern. Biospektrum 28, 481–483 (2022). https://doi.org/10.1007/s12268-022-1810-x
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1810-x