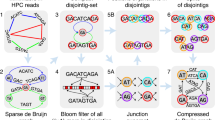
Abstract
Advances in genome sequencing have led to a paradigm shift where project costs are no longer limited by sequencing costs but rather by the computational problems associated with genome assembly. There is an urgent demand for more efficient and accurate methods, in particular for complex genomes. The combination of traditional second and emerging third generation sequencing offers unique benefits. Our own method LazyB enables the resource efficient assembly of low abundant datasets.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Di Genova A, Buena-Atienza E, Ossowski S, Sagot MF (2021) Efficient hybrid de novo assembly of human genomes with WENGAN. Nat Biotechnol 39: 422–430
Haghshenas E, Asghari H, Stoye J et al. (2020) HASLR: fast hybrid assembly of long reads. iScience 23: 101389
Ye C, Hill CM, Wu S et al. (2016). DBG2OLC: efficient assembly of large genomes using long erroneous reads of the third generation sequencing technologies. Sci Rep 6: 1–9
Kececioglu JD, Myers EW (1995) Combinatorial algorithms for DNA sequence assembly. Algorithmica 13: 7–51.
Simpson JT, Wong K, Jackman SD et al. (2009) ABySS: a parallel assembler for short read sequence data. Genome Res 19: 1117–1123
Funding
Funding note: Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Thomas Gatter 2010–2015 Studium Kognitive Informatik und Naturwissenschaftliche Informatik an der Universität Bielefeld. Seit 2015 am Lehrstuhl Bioinformatik der Universität Leipzig. Dort 2022 Promotion unter Anleitung von Prof. Dr. P. F. Stadler.
Peter F. Stadler Bis 1990 Studium der Chemie, Mathematik, Physik und Astronomie an der Universität Wien, Österreich. Dort 1990 Promotion bei Dr. P. Schuster in Chemie. Seit 1994 externes Fakultätsmitglied des Santa Fe Institutes, Santa Fe, USA. 1997–2002 Außerordentlicher Universitätsprofessor an der Universität Wien. Seit 2002 Professor für Bioinformatik an der Universität Leipzig.
Rights and permissions
Open Access: Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Gatter, T., Stadler, P.F. Kosteneffektive hybride Genomassemblierung mit LazyB. Biospektrum 28, 283–286 (2022). https://doi.org/10.1007/s12268-022-1762-1
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1762-1