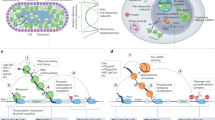
Abstract
Transcription by RNA polymerase II underlies fundamental cellular processes in eukaryotic cells, representing a major regulatory hub in gene expression. Transcription is tightly coupled with co-transcriptional RNA processing to allow the synthesis of functional RNAs. A misregulation can cause human disease. The recent advent of functional multiomics approaches now provides new general insights into the molecular mechanisms that control and link transcription with RNA maturation in cells.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Cramer P (2019) Organization and regulation of gene transcription. Nature 573: 45–54
Vos SM, Farnung L, Boehning M et al. (2018) Structure of activated transcription complex Pol II-DSIF-PAF-SPT6. Nature 560: 607–612
Gonzalez M N, Blears D, Svejstrup J Q (2021) Causes and consequences of RNA polymerase II stalling during transcript elongation. Nat Rev Mol Cell Biol 22: 3–21
Gehring NH, Roignant J (2021) Anything but ordinary — emerging splicing mechanisms in eukaryotic gene regulation. Trends Genet 37: 355–372
Wahl MC, Will CL, Lührmann R (2009) The spliceosome: design principles of a dynamic RNP machine. Cell 136: 701–718
Hanzl A, Winter G W (2020) Targeted protein degradation: current and future challenges. Curr Opin Chem Biol 56: 35–41
Arnold M, Bressin A, Jasnovidova O et al. (2021) A BRD4-mediated elongation control point primes transcribing RNA polymerase II for 3′-processing and termination. Mol Cell 81: 3589–3603
Wu S, Chiang C (2007) The double bromodomain-containing chromatin adaptor Brd4 and transcriptional regulation. J Biol Chem 282: 13141–13145
Valent P, Zuber J (2014) BRD4: a BET (ter) target for the treatment of AML? Cell Cycle 13: 689–690
Winter GE, Mayer A, Buckley DL et al. (2017) BET bromodomain proteins function as master transcription elongation factors independent of CDK9 recruitment. Mol Cell 67: 5–18
Muhar M, Ebert A, Neumann T et al. (2018) SLAM-seq defines direct gene-regulatory functions of the BRD4-MYC axis. Science 360: 800–805
Mayer A, Di Iulio J, Maleri S et al. (2015) Native elongating transcript sequencing reveals human transcriptional activity at nucleotide resolution. Cell 161: 541–554
Funding
Funding note: Open Access funding enabled and organized by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Diese Arbeit wurde durch eine Sachbeihilfe der Deutschen Forschungsgemeinschaft (418415292) unterstützt.
Annkatrin Bressin 2010–2016 Bioinformatikstudium an der FU Berlin. Seit 2017 Doktorandin an der International Max-Planck Research School for Computational Biology and Scientific Computing am Max-Planck-Institut für Molekulare Genetik in Berlin unter Anleitung von Dr. A. Mayer.
Andreas Mayer 2002–2007 Biologiestudium an der LMU München. 2012 Promotion in Biochemie am Genzentrum der LMU unter Anleitung von Dr. P. Cramer. 2012–2016 Postdoktorand an der Harvard Medical School in Boston, MA, USA, im Labor von Dr. L. S. Churchman. Seit Januar 2017 Leiter einer unabhängigen Max-Planck-Forschungsgruppe am Max-Planck-Institut für Molekulare Genetik in Berlin.
Rights and permissions
Open Access: Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Bressin, A., Mayer, A. Neue Einblicke in die Genregulation mittels funktioneller Multiomik. Biospektrum 28, 276–278 (2022). https://doi.org/10.1007/s12268-022-1750-5
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-022-1750-5