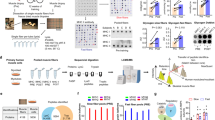
Abstract
Skeletal muscle tissue is composed of different fiber types which differ in their metabolic activity and molecular expression patterns. Mass spectrometric analyses revealed muscle fiber-specific traits but the number of detected proteins is limited due to low protein abundance and high dynamic range. We have developed a new LC-MS/MS method to circumvent the bottleneck of low protein abundance and we have applied this method to measure fiber type-specific phosphoproteomes for the first time.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Spudich J A (2001) The myosin swinging cross-bridge model. Nat Rev Mol Cell Biol 2: 387–392
Bottinelli R, Schiaffino S, Reggiani C (1991) Forcevelocity relations and myosin heavy chain isoform compositions of skinned fibres from rat skeletal muscle. J Physiol 437: 655–672
Schiaffino S, Reggiani C (2011) Fiber types in mammalian skeletal muscles. Physiol Rev 91: 1447–1531
Schiaffino S (2018) Muscle fiber type diversity revealed by anti-myosin heavy chain antibodies. FEBS J 285: 3688–3694
Lang F, Khaghani S, Türk C et al. (2018) Single muscle fiber proteomics reveals distinct protein changes in slow and fast fibers during muscle atrophy. J Proteome Res 17: 3333–3347
Murgia M, Nagaraj N, Deshmukh AS et al. (2015) Single muscle fiber proteomics reveals unexpected mitochondrial specialization. EMBO Rep 16: 387–395
Kallabis S, Abraham L, Müller S et al. (2020) High-throughput proteomics fiber typing (ProFiT) for comprehensive characterization of single skeletal muscle fibers. Skelet Muscle 10: 7
Author information
Authors and Affiliations
Corresponding author
Additional information
Funding note
Open Access funding enabled and organized by Projekt DEAL.
Sebastian Kallabis 2011–2015 Bachelorstudium Biologie, Universität zu Köln. 2015–2017 Masterstudium Biologie, Universität zu Köln. Seit 2017 Doktorand im CECAD Forschungszentrum, Universität zu Köln.
Marcus Krüger 1991–1997 Diplom Chemie & Biologie, TU Braunschweig. 1998–2004 Promotion/Postdoc, Universität Halle-Wittenberg. 2004–2005 Postdoc, Universität Süddänemark, Odense, Dänemark. 2005–2007 Postdoc, Max-Planck-Institut für Biochemie, Martinsried. 2008–2014 Proteomics Facilityleiter, Max-Planck-Institut für Herz- und Lungenforschung, Bad Nauheim. Seit 2014 Professor, Institut für Genetik/CECAD, Universität zu Köln.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Kallabis, S., Krüger, M. ProFiT: eine MS-basierte Methode zur Skelettmuskelfasertypisierung. Biospektrum 27, 719–722 (2021). https://doi.org/10.1007/s12268-021-1671-8
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-021-1671-8