Abstract
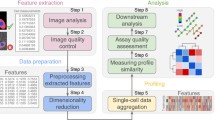
Genes that share a distinct phenotype often share biological functions. A principle that is used in genetic screens and that provides the basis for our understanding of key biological processes. Traditionally, individual phenotypes were used to group mutant alleles into cellular pathways. Today, high-throughput technologies allow the screening of thousands of perturbations. Using computational methods and machine learning, millions of images are profiled to assign biological effects to genes and drugs.
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Mendel G (1866) Versuche über Pflanzenhybriden. Verhandlungen des Naturforschenden Vereines in Brünn 4: 3–47
Nüsslein-Volhard C, Wieschaus E (1980) Mutations affecting segment number and polarity in Drosophila. Nature 287: 795–801
Jorgensen EM, Mango SE (2002) The art and design of genetic screens: caenorhabditis elegans. Nat Rev Genet 3: 356–369
Boutros M, Heigwer F, Laufer C (2015) Microscopy-based high-content screening. Cell 163: 1314–1325
Caicedo JC, Singh S, Carpenter AE (2016) Applications in image-based profiling of perturbations. Curr Opin Biotechnol 39: 134–142
Kiger AA, Baum B, Jones S et al. (2003) A functional genomic analysis of cell morphology using RNA interference. J Biol 2: 27
Heigwer F, Scheeder C, Miersch T et al. (2018) Time-resolved mapping of genetic interactions to model rewiring of signaling pathways. Elife 7: e40174
Breinig M, Klein FA, Huber W, Boutros M (2015) A chemical-genetic interaction map of small molecules using high-throughput imaging in cancer cells. Mol Syst Biol 11: 846
Ziegler S, Sievers S, Waldmann H (2021) Morphological profiling of small molecules. Cell Chem Biol 28: 300–319
Gibson CC, Zhu W, Davis CT et al. (2015) Strategy for identifying repurposed drugs for the treatment of cerebral cavernous malformation. Circulation 131: 289–299
Scheeder C, Heigwer F, Boutros M (2018) Machine learning and image-based profiling in drug discovery. Curr Opin Syst Biol 10: 43–52
Laufer C, Fischer B, Billmann M et al. (2013) Mapping genetic interactions in human cancer cells with RNAi and multiparametric phenotyping. Nat Methods 10: 427–431
Fischer B, Sandmann T, Horn T et al. (2015) A map of directional genetic interactions in a metazoan cell. ELife 4: e05464
Port F, Strein C, Stricker M et al. (2020) A large-scale resource for tissue-specific CRISPR mutagenesis in Drosophila. Elife 9: e53865
Renner H, Grabos M, Becker KJ et al. (2020) A fully automated high-throughput workflow for 3D-based chemical screening in human midbrain organoids. Elife 9: e52904
Ruiz M, Bodhicharla R, Svensk E et al. (2018) Membrane fluidity is regulated by the C. elegans transmembrane protein FLD-1 and its human homologs TLCD1/2. Elife 7: e40686
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Wir danken dem Team des Boutros-Labors für hilfreiche Kommentare zum Manuskript. Die Forschung im Labor von M. B. wurden durch einen Grant von GSK, einen ERC Advanced Grant (“Syngene”) und ERC Synergy Grant (“Decode”) der Europäischen Kommission und dem SFB 1324 der Deutschen Forschungsgemeinschaft unterstützt.
Funding note
Open Access funding enabled and organized by Projekt DEAL.
Christian Scheeder Studium der Molekularen Biotechnologie an den Universitäten Heidelberg, Karlsruhe und Kopenhagen, Dänemark. Seit 2016 Promotionsstudent an der Universität Heidelberg in der Gruppe von Prof. Dr. M. Boutros.
Florian Heigwer Studium der Molekularen Biotechnologie an den Universitäten Heidelberg und Stockholm, Schweden. 2013–2018 Promotion an der Universität Heidelberg. Seit 2018 Postdoktorand in der Gruppe von Prof. Dr. M. Boutros.
Michael Boutros Studium der Biochemie und Biologie. 1999 Promotion am EMBL, Heidelberg. 1999–2003 Postdoktorand an der Harvard Medical School, Boston, USA. 2003–2008 Emmy-Noether-Gruppenleiter am Deutschen Krebsforschungszentrum (DKFZ). Seit 2008 Abteilungsleiter im Bereich Genomforschung am DKFZ und Professor für Zellund Molekularbiologie an der Universität Heidelberg. Seit 2020 Direktor des Marsilius Kollegs an der Universität Heidelberg und 2021 Sprecher des Sonderforschungsbereichs SFB1324.
Rights and permissions
Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Scheeder, C., Heigwer, F. & Boutros, M. Analyse von Zellfunktionen mit Hochdurchsatz-Mikroskopie und KI. Biospektrum 27, 607–610 (2021). https://doi.org/10.1007/s12268-021-1648-7
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-021-1648-7