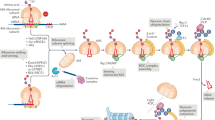
Abstract
Newly synthesized proteins are processed by a variety of ribosome-associated factors that regulate cotranslational protein folding, transport and degradation. How these competing factors gain regulated and timely access to ribosomes and specific nascent substrates is poorly understood. Recent studies identified a key factor in eukaryotes that coordinates multiple cotranslational events at the ribosomal tunnel exit — the nascent polypeptide-associated complex (NAC).
Article PDF
Similar content being viewed by others
Avoid common mistakes on your manuscript.
Literatur
Deuerling E, Gamerdinger M, Kreft SG (2019) Chaperone interactions at the ribosome. Cold Spring Harb Perspect Biol 11, doi: https://doi.org/10.1101/cshperspect.a033977
Wiedmann B, Sakai H, Davis TA et al. (1994) A protein complex required for signal-sequence-specific sorting and translocation. Nature 370:434–440
Gamerdinger M, Kobayashi K, Wallisch A et al. (2019) Early scanning of nascent polypeptides inside the ribosomal tunnel by NAC. Mol Cell 75:996–1006
Walter P (1994) Signal sequence recognition and protein targeting to the endoplasmic reticulum membrane. Annu Rev Cell Biol 10:87–119
Gamerdinger M, Hanebuth MA, Frickey T et al. (2005) The principle of antagonism ensures protein targeting specificity at the endoplasmic reticulum. Science 348:201–207
Neupert W, Herrmann JM (2007) Translocation of proteins into mitochondria. Annu Rev Biochem 76:723–749
Williams CC, Jan CH, Weissman JS (2014) Targeting and plasticity of mitochondrial proteins revealed by proximity-specific ribosome profiling. Science 346:748–751
Lesnik C, Cohen Y, Atir-Lande A et al. (2014) OM14 is a mitochondrial receptor for cytosolic ribosomes that supports co-translational import into mitochondria. Nat Commun 5:5711
Shen K, Gamerdinger M, Chan R et al. (2019) Dual role of ribosome-binding domain of NAC as a potent suppressor of protein aggregation and aging-related proteinopathies. Mol Cell 74:729–741
Funding
Funding: Open Access funding provided by Projekt DEAL.
Author information
Authors and Affiliations
Corresponding author
Additional information
Danksagung
Die Autoren danken der DFG für die Unterstützung im Rahmen des SFB969 und C. Schlatterer und E. Oberer-Bley für ihre Hilfe bei der Erstellung des Manuskripts.
Martin Gamerdinger 1999–2009 Biologiestudium und Promotion am Institut für Pathobiochemie an der Universität Mainz unter Anleitung von Prof. Dr. C. Behl. 2009–2011 Postdoktorand an der Universität Mainz. 2012–2015 Postdoktorand an der Universität Konstanz im Labor von Prof. Dr. E. Deuerling. Seit 2016 unabhängiger Nachwuchsgruppenleiter an der Universität Konstanz.
Karina Gense 2010–2016 Life-Science-Studium an der Universität Konstanz. Seit 2016 Promotion am Lehrstuhl für Molekulare Mikrobiologie unter Anleitung von Prof. Dr. E. Deuerling, Universität Konstanz.
Rights and permissions
Open Access: Dieser Artikel wird unter der Creative Commons Namensnennung 4.0 International Lizenz veröffentlicht, welche die Nutzung, Vervielfältigung, Bearbeitung, Verbreitung und Wiedergabe in jeglichem Medium und Format erlaubt, sofern Sie den/die ursprünglichen Autor(en) und die Quelle ordnungsgemäß nennen, einen Link zur Creative Commons Lizenz beifügen und angeben, ob Änderungen vorgenommen wurden. Die in diesem Artikel enthaltenen Bilder und sonstiges Drittmaterial unterliegen ebenfalls der genannten Creative Commons Lizenz, sofern sich aus der Abbildungslegende nichts anderes ergibt. Sofern das betreffende Material nicht unter der genannten Creative Commons Lizenz steht und die betreffende Handlung nicht nach gesetzlichen Vorschriften erlaubt ist, ist für die oben aufgeführten Weiterverwendungen des Materials die Einwilligung des jeweiligen Rechteinhabers einzuholen. Weitere Details zur Lizenz entnehmen Sie bitte der Lizenzinformation auf http://creativecommons.org/licenses/by/4.0/deed.de.
About this article
Cite this article
Gense, K., Gamerdinger, M. Ordnung am Ribosom — der multifunktionale Komplex NAC. Biospektrum 26, 248–251 (2020). https://doi.org/10.1007/s12268-020-1367-5
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-020-1367-5