Abstract
In-depth structural and mechanistic analysis of biomolecular complexes is crucial for modern life sciences. Here we give an overview on hydrogendeuterium exchange mass spectrometry (HDX-MS) as an attractive tool to study the dynamic and structural features of proteins and their complexes.
Similar content being viewed by others
Change history
22 December 2017
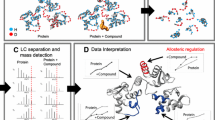
Bei der Produktion der bereits veröffentlichten Originalversion des Artikels ist ein Fehler in der Legende zu Abbildung 1 entstanden. Die Farbbezeichnungen bei Wasserstoff (blau) und Deuterium (rot) waren vertauscht. Anbei finden Sie die korrigierte Version.
Literatur
Bai Y, Milne JS, Mayne L et al. (1994) Protein stability parameters measured by hydrogen exchange. Proteins 20:4–14
Engen JR, Wales TE (2015) Analytical aspects of hydrogen exchange mass spectrometry. Annu Rev Anal Chem 8:127–148
Pirrone GF, Iacob RE, Engen JR (2015) Applications of hydrogen/deuterium exchange MS from 2012 to 2014. Anal Chem 87:99–118
Englander SW, Mayne L (2017) The case for defined protein folding pathways. Proc Natl Acad Sci USA 114:8253–8258
Pantazatos D, Kim JS, Klock HE et al. (2004) Rapid refinement of crystallographic protein construct definition employing enhanced hydrogen/deuterium exchange MS. Proc Natl Acad Sci USA 101:751–756
Masson GR, Jenkins ML, Burke JE (2017) An overview of hydrogen deuterium exchange mass spectrometry (HDX-MS) in drug discovery. Expert Opin Drug Discov 12:981–994
Schaper S, Steinchen W, Krol E et al. (2017) AraC-like transcriptional activator CuxR binds c-di-GMP by a PilZ-like mechanism to regulate extracellular polysaccharide production. Proc Natl Acad Sci USA 114:E4822–E4831
Steinchen W, Schuhmacher JS, Altegoer F et al. (2015) Catalytic mechanism and allosteric regulation of an oligomeric (p)ppGpp synthetase by an alarmone. Proc Natl Acad Sci USA 112:13348–13353
Iacob RE, Engen JR (2012) Hydrogen exchange mass spectrometry: are we out of the quicksand? J Am Soc Mass Spectrom 23:1003–1010
Author information
Authors and Affiliations
Corresponding author
Additional information
Wieland Steinchen Pharmaziestudium an der Universität Jena. 2017 Promotion bei Dr. G. Bange an der Universität Marburg. Seit 2017 wissenschaftlicher Mitarbeiter am DFG-geförderten „Marburger Gerätezentrum für Interaktion, Dynamik und Struktur biomolekularer Komplexe“ unter der Leitung von Dr. G. Bange.
Uwe Linne Chemiestudium an der Universität Marburg. Promotion und Postdoc bei Prof. Dr. M. A. Marahiel. Seit 2010 Leiter der Abteilung Massenspektrometrie am Fachbereich Chemie der Universität Marburg.
Gert Bange Biochemiestudium an der Universität Halle/Saale. Promotion und Postdoc bei Prof. Dr. I. Sinning an der Universität Heidelberg. 2013 Etablierung einer Arbeitsgruppe am LOEWE-Zentrum für Synthetische Mikrobiologie (SYNMIKRO) und am Fachbereich Chemie der Universität Marburg.
Ein Erratum zu diesem Beitrag ist unter https://doi.org/10.1007/s12268-018-0880-2 zu finden.
Rights and permissions
About this article
Cite this article
Steinchen, W., Linne, U. & Bange, G. HDX-MS in den Lebenswissenschaften. Biospektrum 23, 772–775 (2017). https://doi.org/10.1007/s12268-017-0871-8
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-017-0871-8